ชื่องานวิจัยภาษาไทย
การวิเคราะห์การแสดงออกของยีนที่เกิดจาก 6-OHDA และรีเซอร์พีน ต่อระบบประสาทและการเปลี่ยนแปลงพฤติกรรมในแบบจำลอง Caenorhabditis elegans
Highlight
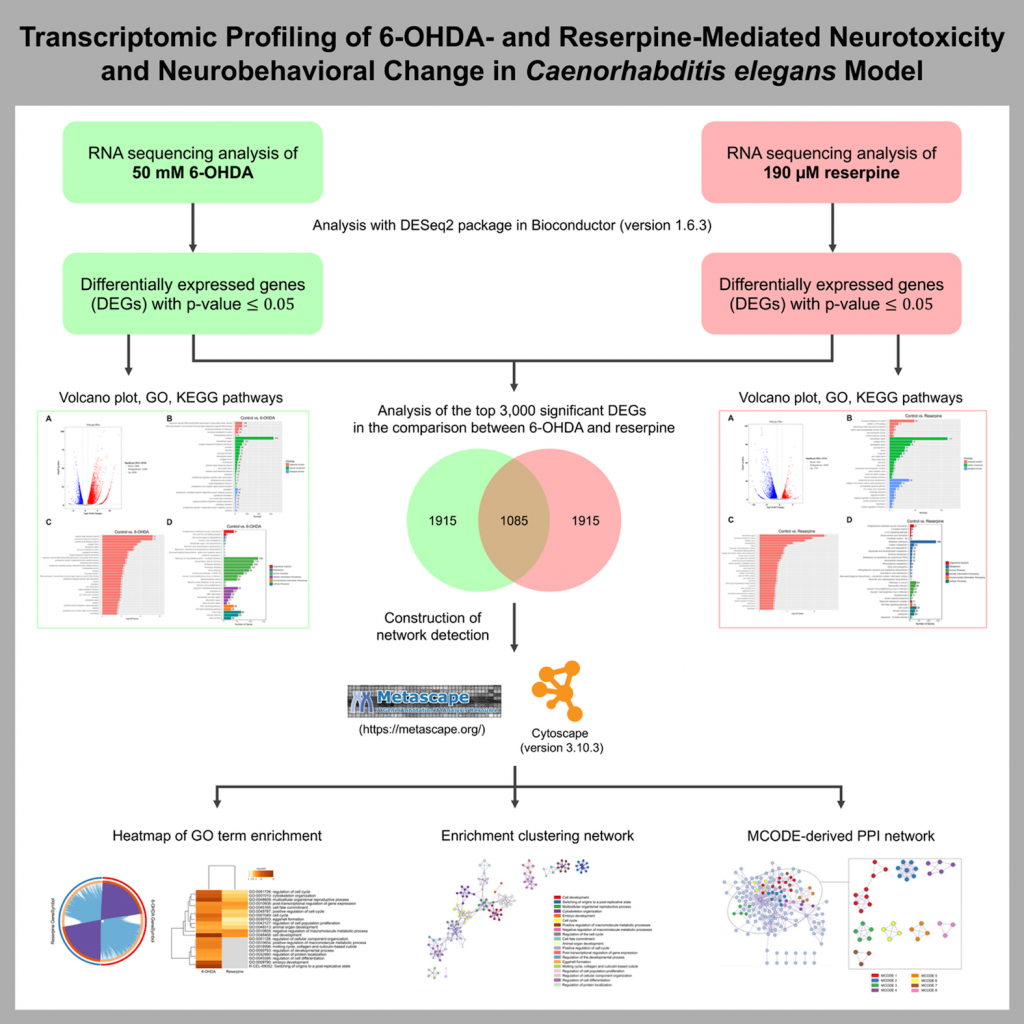
สาร 6-OHDA และ reserpine ก่อให้เกิดความเป็นพิษต่อระบบประสาทผ่านกลไกระดับยีนที่แตกต่างกันในหนอน Caenorhabditis elegans โดย 6-OHDA ส่งผลต่อกระบวนการสร้างและสลายโปรตีน ขณะที่ reserpine ส่งผลต่อระบบสารสื่อประสาทและเมแทบอลิซึม งานวิจัยนี้ได้แสดงให้เห็นการเปลี่ยนแปลงระดับยีนที่เกี่ยวข้องกับการเสื่อมของเซลล์ประสาทและการเปลี่ยนแปลงพฤติกรรม ซึ่งเป็นข้อมูลสำคัญต่อความเข้าใจโรคพาร์กินสัน
ที่มาและความสำคัญ
สารพิษต่อระบบประสาท เช่น 6-hydroxydopamine (6-OHDA) และ reserpine ถูกใช้เป็นแบบจำลองในการศึกษากลไกการเกิดโรคทางระบบประสาท โดยเฉพาะโรคพาร์กินสัน อย่างไรก็ตาม กลไกระดับโมเลกุลที่เกี่ยวข้องกับความเป็นพิษและการเปลี่ยนแปลงพฤติกรรมจากสารทั้งสองชนิดยังไม่ชัดเจน การศึกษานี้ใช้หนอนตัวกลม Caenorhabditis elegans เป็นแบบจำลอง และวิเคราะห์การแสดงออกของยีนระดับทรานสคริปโตม เพื่อทำความเข้าใจกลไกการออกฤทธิ์ที่เกี่ยวข้อง ผลการศึกษาจะช่วยเพิ่มองค์ความรู้เกี่ยวกับกลไกการเสื่อมของเซลล์ประสาท และเป็นข้อมูลพื้นฐานสำคัญต่อการพัฒนาแนวทางป้องกันหรือรักษาโรคทางระบบประสาทในอนาคต
Abstract
Neurotoxic agents such as 6-hydroxydopamine (6-OHDA) and reserpine are reported to cause neurodegenerative and neuroendocrine effects, respectively. Using the Caenorhabditis elegans (C. elegans) model, this study performs comparative transcriptomic profiling to elucidate molecular pathways that contribute to their neurotoxicity. Differentially expressed genes (DEGs) were identified following 6-OHDA and reserpine exposure, with subsequent analyses for Gene Ontology (GO) and KEGG pathway enrichment. Notably, 6-OHDA mainly disrupted ribosomal/proteasomal activity and neurodegeneration-related pathways, while reserpine primarily affected the extracellular compartment, neuropeptide-based signaling, and metabolic processes. Meta-analysis of the top 3,000 DEGs, combined with comparative enrichment network analysis of the 2 neurotoxicants using Metascape, identified critical regulatory processes, including cell development, reproduction, cytoskeletal organization, cell cycle control, metabolic pathways, and post-transcriptional regulation. In addition, protein-protein interaction (PPI) network analysis revealed eight distinct Molecular Complex Detection (MCODE) modules, which correspond to biological clusters such as regulation of translation, fatty acid metabolism, glutamate/glutamine metabolism, ceramide metabolism, sphingolipid metabolism, porphyrin metabolism, and post-transcriptional regulation. Moreover, reserpine exposure altered neurobehavioral function in the ethanol avoidance assay without inducing dopaminergic (DAergic) neurodegeneration in C. elegans. Overall, these findings suggest a transcriptomic framework that reports both common and unique molecular signatures of neurotoxicant-mediated neurodegeneration and behavioral alterations. These results provide valuable insights for future studies on regulatory pathways involved in PD pathogenesis.
KEYWORDS: Transcriptome, Metascape, 6-OHDA, Reserpine, Neurotoxicity, Caenorhabditis elegans
Citation: Promtang S*, Sanguanphun T, Rodma D, Sunan R, Sayinta A, Fuangfoo T, Snitmatjaro N, Chaichantipyuth C, Kamkaen N, Meemon K, Chalorak P. Transcriptomic Profiling of 6-OHDA- and Reserpine-Mediated Neurotoxicity and Neurobehavioral Change in Caenorhabditis elegans Model. Trends Sci. 2026;23(4):11920. DOI: https://doi.org/10.48048/tis.2026.11920.
RELATED SDGs:
3. GOOD HEALTH AND WELL-BEING

ผู้ให้ข้อมูล: รองศาสตราจารย์ ดร.ไกร มีมล
ชื่ออาจารย์ที่ทำวิจัย: รองศาสตราจารย์ ดร.ไกร มีมล
ชื่อนักศึกษาที่ทำวิจัย: Sukrit Promtang
แหล่งทุนวิจัย: Pathumthani University and Mahidol University
Credit ภาพ: รองศาสตราจารย์ ดร.ไกร มีมล
Tags: 6-OHDA, Caenorhabditis elegans, Metascape, Neurotoxicity, Reserpine, Transcriptome
